DNA“幸运星”,同时检测与抑制病毒
用手工纸折出五颜六色的幸运星,一定是很多人年少时的美好记忆,可能一些读者还收藏着一罐由重要的Ta折给自己的幸运星。
图片来源于网络
今天,对于化学家而言,幸运星不仅仅可以用纸折叠得到,也可以用分子折叠获得。随着DNA纳米技术的发展,这种由脱氧核糖核酸组成的聚合物对于化学家的意义早已不再仅仅是承载生命信息的密码。编码的重组以及空间结构的定向折叠能够赋予DNA很多神奇的性质,形成具有催化活性、识别特性、机械性能的DNA元件。将这些DNA元件互相组装形成复杂的纳米结构,将形成具有一定机械性能的纳米机器。
近期,Nature Chemistry 上发表了一项由南京邮电大学与伦斯勒理工大学的研究者合作的研究论文,报道了一种由DNA片段利用碱基互补配对相互折叠,构成五角星形DNA纳米结构的组装策略,所得到的结构被称为DNA纳米星(DNA star)。这一DNA纳米星中嵌入了可以识别登革热病毒表面配体的适配体(Aptamer),使这一DNA纳米星能够在血液中高选择性地与登革热病毒结合,产生荧光信号用于检测的同时,抑制病毒的活性,达到检测与抑制病毒的双重作用(笔者慨叹,不知道这种技术有没有希望用于解决如今新型冠状病毒的快速、高灵敏度、高特异性检测与抑制的难题)。
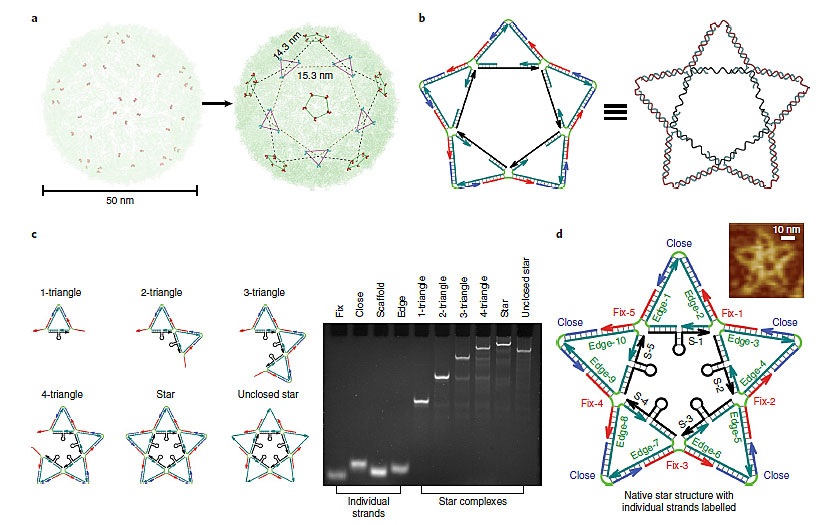
图1. (a) 登革热病毒表面ED3的分布规律;(b-d) DNA纳米星的结构、构成方式、凝胶电泳、结构域。图片来源:Nat. Chem.
对登革热病毒表面的包膜蛋白结构域III(ED3)进行空间分布的解析发现,其在分布于五边形的顶点上,可以用五角星的端点及内角覆盖。基于这样的分布特征,研究人员设计了五角星型的DNA纳米结构,其DNA杂交方法及构成步骤如图X所示。凝胶电泳显示,得益于精确控制的杂交过程,DNA纳米星的构成率可以达到88.1%。该DNA纳米星的内边由五个亚稳态的茎-环结构组成,使其存在一定的可塑性。在特定的外在信号刺激下,能够发生构象的变化使茎-环结构打开,导致DNA纳米星五个角的角度变大。
在DNA纳米星的结构中,星形内部柔性、二价的六边形对于它的传感特性具有重要的意义。该结构一方面为DNA纳米星的结构稳定性提供支撑,另一方面也为其提供了构象的变化能力,从而产生传感信号。很有趣的是,研究者发现DNA纳米星中用来与ED3结合的适配体的分布位置,对于DNA纳米星与登革热病毒的结合具有很大的影响。研究者设计了结构相似的DNA纳米五角星、六芒星、七角星等,其中只有五角星可以实现与ED3空间分布的一一对应。结果发现,六芒星、七角星等结构类似的DNA纳米星虽然也能识别ED3,但是因为欠缺了空间结构上的特异性对应关系,在检测登革热病毒时根据荧光信号获得的检测灵敏度就会显著下降。这一现象说明,根据目标物的空间分布规律,设计对应的DNA纳米结构,对于构建纳米传感器具有重要意义。
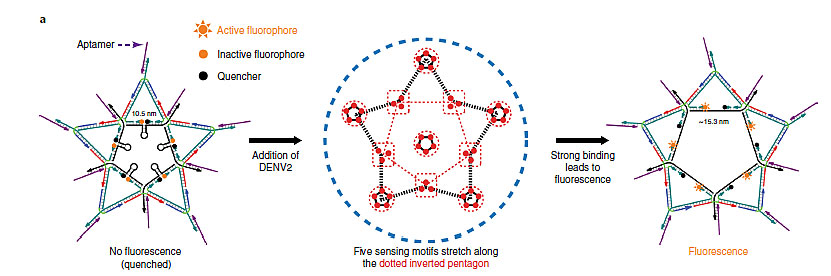
图2. DNA纳米星与登革热病毒结合后构象的变化以及荧光增强的原理。图片来源:Nat. Chem.
更加神奇的结果在于,DNA纳米星不仅能够实现对登革热病毒的检测,还能对其产生抑制作用。DNA纳米星对ED3的结合将会极大抑制病毒的复制,且抑制能力与结合能力密切相关。与检测部分的结果相类似,DNA纳米五角星因为所有位点均与ED3的分布具有空间对应性,对病毒的抑制能力也最强。而其它结构,诸如DNA纳米六芒星、七角星,以及其它含有ED3的适配体元件,随着空间匹配度的降低,对病毒的抑制能力也依次降低。该结果说明,在利用适配体实现对目标的结合或者抑制时,增加空间位置上的匹配度,将极大提高结合能力。
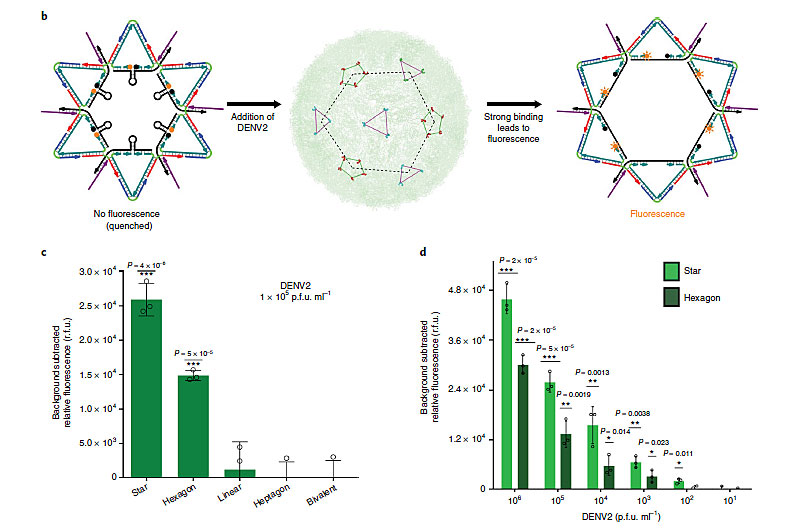
图3. DNA纳米六芒星的结构,以及其它DNA纳米结构对登革热病毒的抑制能力。图片来源:Nat. Chem.
在文章的最后,作者也对设计与目标物具有空间对应性的DNA纳米结构的策略进行了论述。主要有以下步骤:(1)选择合适的连接物;(2)研究目标物的分布特征;(3)设计DNA纳米结构匹配目标物的分布特征;(4)将连接物嵌入DNA纳米结构中;(5)对识别模式进行调节,设计多种几何结构进行识别。
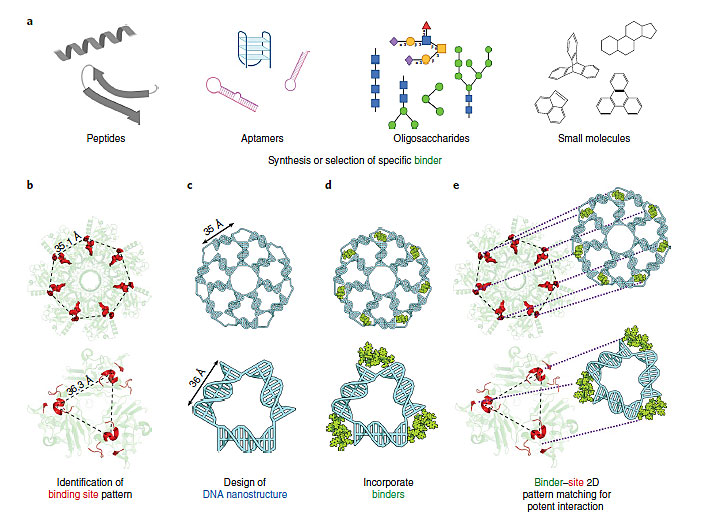
图4. 基于DNA纳米结构对配体的空间对应性进行设计的方法。图片来源:Nat. Chem.
该文章不仅创造了一种新型的DNA纳米结构,将这种柔性可变的DNA纳米骨架应用于病毒的检测与抑制,更重要的是提出了一种提高已知配体对目标物的结合能力的策略。实际研究中,当确定了目标物后,用于实现结合的配体往往种类有限,结合能力很难提高。这种情况下,利用DNA纳米结构对配体的空间位置进行操控,而实现提高对目标物的结合能力,对于分析检测、医药研究等领域都有重要意义。可以预见在不远的将来,这一技术可能会应用于细胞表面蛋白的检测。
原文(扫描或长按二维码,识别后直达原文页面,或点此查看原文):

Designer DNA architecture offers precise and multivalent spatial pattern-recognition for viral sensing and inhibition
Paul S. Kwon, Shaokang Ren, Seok-Joon Kwon, Megan E. Kizer, Lili Kuo, Mo Xie, Dan Zhu, Feng Zhou, Fuming Zhang, Domyoung Kim, Keith Fraser, Laura D. Kramer, Nadrian C. Seeman, Jonathan S. Dordick, Robert J. Linhardt, Jie Chao, Xing Wang
Nat. Chem., 2020, 12, 26–35, DOI: 10.1038/s41557-019-0369-8
(本文由传光簇供稿)
如果篇首注明了授权来源,任何转载需获得来源方的许可!如果篇首未特别注明出处,本文版权属于 X-MOL ( x-mol.com ), 未经许可,谢绝转载!




























 京公网安备 11010802027423号
京公网安备 11010802027423号